Page 42 - 《中国药科大学学报》2026年第2期
P. 42
168 学报 Journal of China Pharmaceutical University 2026, 57(2): 163 − 171 第 57 卷
去除水分子
去除小分子
确定活性位点
分子
加氢
对接
结构优化
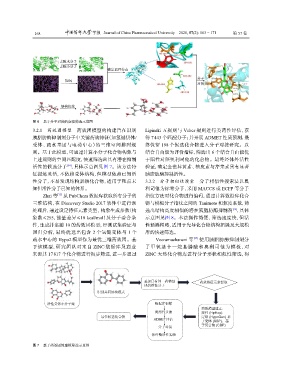
图 6 基于分子对接的虚拟筛选示意图
3.2.1 药效团模型 药效团模型的构建旨在识别 Lipinski 五规则与 Veber 规则进行类药性评估,获
胰脂肪酶抑制剂分子中关键药效特征(如氢键供体/ 得 7 443 个匹配分子;并开展 ADMET 性质预测,最
受体、疏水基团与电荷中心)的三维空间排列规 终保留 198 个候选化合物进入分子对接研究。以
则。基于此模型,可通过计算小分子化合物构象与 结合自由能为评价指标,筛选出 6 个结合自由能优
上述规则的空间匹配度,快速筛选出具有潜在抑制 于阳性对照奥利司他的化合物。最终经体外活性
活性的候选分子 ,具体示意图见图 7。该方法特 验证,确定金雀异黄素、柚皮素与芹菜素具有显著
[34]
征提炼灵活,不依赖受体结构,但模型依赖已知活 胰脂肪酶抑制活性。
性分子,不易发现结构新颖化合物,适用于靶点未 3.2.2 分子相似性搜索 分子相似性搜索法以奥
知但活性分子已知的体系。 利司他为标签分子,采用 MACCS 或 ECFP 等分子
Zhai 等 [35] 从 PubChem 数据库获取所有分子的 指纹方法对化合物进行编码,通过计算数据库化合
三维结构,在 Discovery Studio 2017 软件中进行预 物与模板分子指纹之间的 Tanimoto 相似度系数,筛
处理后,通过设定特征元素类型、构象生成参数(构 选出结构高度相似的潜在胰脂肪酶抑制剂 ,具体
[36]
象数≤255,能量差异≤10 kcal/mol)及分子叠合条 示意图见图 8。本法操作简便、筛选速度快,但活
件,生成排名前 10 的药效团模型;经测试集验证与 性预测粗略,适用于先导化合物结构拓展及大规模
回归分析,最终优选出包含 2 个氢键受体与 1 个 库的快速筛选。
疏水中心的 Hypo2 模型作为最优三维药效团。基 Veeramachaneni 等 [37] 使用胰脂肪酶抑制剂分
于该模型,研究团队对来自 ZINC 数据库及商业 子甲氧基十一烷基膦酸和奥利司他为模板,对
来源共 17 817 个化合物进行初步筛选,进一步通过 ZINC 天然化合物库进行分子形状相似性筛选,得
叠加具有同一药物基 药效特征元素提取
团的活性分子
识别共同结构模式
. . . . . .
活性受体小分子集 数据库初筛
药效模型建立:
类药性过滤 定性 (HpHop).
最佳候选化合物 定量 (HypoGen) 基
ADMET评估 于受体 (SBP),基
于复合物 (CBP)
分子对接
体外酶活性实验
图 7 基于药效团的虚拟筛选示意图