Page 172 - 《水产学报》2025年第11期
P. 172
杨锦毅,等 水产学报, 2025, 49(11): 119314
256 257 259 260 260 261 261 262 262 262 263 264
250
200 230 232 235 237 238 239 240 242 242 244 246
217 225
并集大小/种 union size 100
0
(a)
232 COⅠ−PS1
223 12S−Tele02
207 12S−Mifish−U
200 12S−AcDBM07
196 16S−Ac16s
200 0 数据集组合方式
数据集大小/种 set composition
set size (c)
(b)
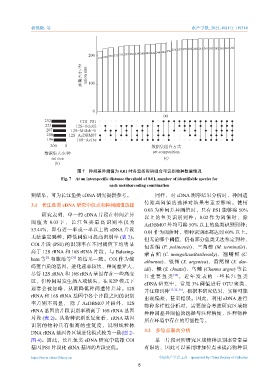
图 7 种间差异阈值为 0.01 时各宏条形码组合可识别物种数量情况
Fig. 7 At an interspecific distance threshold of 0.01, number of identifiable species for
each metabarcoding combination
别结果,可为长江鱼类 eDNA 研究提供参考。 同样,对 eDNA 测序结果分析时,种间遗
传距离阈值的选择对结果有重要影响。使用
3.1 长江鱼类 eDNA 研究中位点和种间阈值选择
0.03 为种间差异阈值时,只有 PS1 能够将 50%
研究表明,单一的 eDNA 片段在种间差异
以上的鱼类识别到种;0.02 作为阈值时,除
阈 值 为 0.03 下 , 长 江 鱼 类 最 高 识 别 率 仅 为
AcDBM07 外均可将 50% 以上的鱼类识别到种;
53.44%,即有近一半或一半以上的 eDNA 片段
0.01 作为阈值时,物种识别率都达到 60% 以上。
无法鉴定到种,降低阈值可提高识别率 (表 2)。
但无论哪个阈值,仍有部分鱼类无法鉴定到种,
COI 片段 (PS1) 的识别率在不同阈值下均明显
包括鳊 (P. pekinensis)、三角鲂 (M. terminalis)、
高于 12S rRNA 和 16S rRNA 片段,与 Balasing-
蒙 古 鲌 (C. mongolicusBasilewsky)、 翘 嘴 鲌 (C.
[3]
ham 等 和陈治等 [35] 的结果一致。COI 作为编
alburnus)、银鲴 (X. argentea)、黄尾鲴 (X. dav-
码蛋白质的基因,进化速率较快、种间差异大,
idi)、鳜 (S. chuatsi)、乌鳢 (Channa argus) 等长
尽管 12S rRNA 和 16S rRNA 基因存在一些高变
江 重 要 鱼 类 [24] 。 近 年 发 表 的 一 些 长 江 鱼 类
区,但种间易发生插入或缺失,在 K2P 模式下
eDNA 研究中,常用 3% 阈值进行 OTU 聚类,
通常会被忽略,从而降低种间遗传差异。12S [13, 22, 36]
并注释到种 ,根据本研究结果,实际可能
rRNA 和 16S rRNA 基因中各个片段之间的识别
出现偏差,甚至错误。因此,利用 eDNA 进行
率差别不明显, 除了 AcDBM07 片段外,12S
物种多样性分析时,需要综合考虑研究区域物
rRNA 基因的片段识别率稍高于 16S rRNA 基因
种种间差异阈值的选择与注释精度、注释物种
片段 (表 2)。从物种识别重复度看,rRNA 基因
所在环境中存在的可能性等。
识别的物种具有很高的重复度,说明线粒体
3.2 多位点联合分析
DNA rRNA 基因各区域进化模式较为一致(图 2~
图 4)。因此,长江鱼类 eDNA 研究中选择 COI 单一片段对所研究区域物种识别率常常是
基因 PS1 片段比 rRNA 基因的片段更优。 有限的,因此可以采用增加位点来提高物种识
https://www.china-fishery.cn 中国水产学会主办 sponsored by China Society of Fisheries
8