Page 19 - 《渔业研究》2026年第1期
P. 19
16 渔 业 研 究 第 48 卷
最为严格和保守的一种方法 [15] ,将单次检验的显 文献检索结果,注释候选基因的生物学功能,筛选
著性 P 值 0.05 除以多重比较的次数(在 GWAS 中 与目标性状相关的候选功能基因。
为 SNP 位点的个数)作为校正后的阈值,将各位
2 结果
点的 P 值与之进行比较,如果某位点的 P 值小于
校正阈值,则可判别该位点与性状之间存在显著性 2.1 表型性状描述性统计
关联。根据 GWAS 分析结果绘制 Quantile-Quantile 本研究所用乌鳢样品的体质量和全长性状的描
(QQ)plot 和曼哈顿图。 述性统计结果参见表 1,所用乌鳢全长为 16.61~
1.5 候选基因鉴定及功能分析 27.22 cm,平均值为 20.92 cm,变异系数为 7.28;
筛选表型 P 值小于 0.05 的位点,利用已发表的 体质量为 22.66~180.66 g,平均值为 77.13 g,变异
乌鳢基因注释信息,扫描显著性位点上下游 50 kb 系数为 24.29。统计分析显示,乌鳢的体质量和全
的序列,查找潜在候选基因。根据 NCBI 数据库和 长性状数据呈近正态分布。
表 1 乌鳢表型性状
Tab. 1 Descriptive statistics of C. argus
性状 最大值 最小值 中位数 平均值 标准差 变异系数/%
Traits Max Min Median Mean SD CV
全长 Total length 27.22 16.61 20.91 20.92 1.52 7.28
体质量 Body mass 180.66 22.66 75.55 77.13 18.73 24.29
2.2 SNP 分型 根据 EMMAX 软件结果和 Bonferroni 校正 P 值,
对 Super-GBS 技术简化基因组测序的数据进行 得到乌鳢全长和体质量曼哈顿图(图 3 和图 4) 。
进一步过滤,保留 Reads 支持深度不小于 4 的位 全长和体质量性状未找到 Bonferroni 校正后的阈值
点,去除 MAF<0.01 的位点,保留 80% 的个体能 线以上显著关联的 SNP 位点,但经 FDR 校正后,
够分型的位点。过滤后得到 47 536 个 SNP 位点, 找到了 3 个与体质量性状显著关联的 SNP 位点。
用于乌鳢表型性状的 GWAS 分析。
2.3 全基因组关联分析 5
根据 EMMAX 软件运行结果,得到每个 SNP
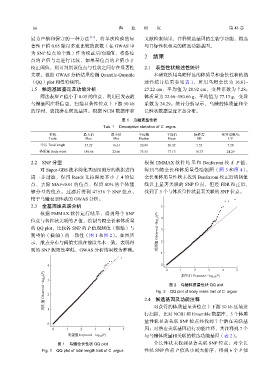
位点与各性状关联的 P 值,绘制乌鳢全长和体质量 4
的 QQ plot,比较各 SNP 的 P 值观测值(纵轴)与 3
期望值(横轴)的一致性(图 1 和图 2) 。如图所 观测值 Observed −log 10 (P)
示,散点分布与阈值实线在前段基本一致,表明得 2
到的 SNP 假阳性率低,GWAS 分析结果较为准确。
1
4 0
3
0 1 期望值 Expected −log 10 (P) 4 5
2
观测值 Observed −log 10 (P) 2 2.4 候选基因及功能注释 QQ plot
3
图 2 乌鳢体质量性状
Fig. 2 QQ plot of body mass trait of C. argus
对获得的体质量显著位点上下游
50 kb
1
个体质
行扫描,比对 NCBI 和 Ensemble 数据库,3 区域进
量性状显著关联 SNP 位点共找到 7 个潜在关联基
0
0 1 2 3 4 5 因;对潜在关联基因进行功能注释,共注释到 7 个
期望值 Expected −log 10 (P) 与乌鳢体质量相关联的候选功能基因(表 2) 。
图 1 乌鳢全长性状 QQ plot 全长性状未找到显著关联 SNP 位点;对全长
Fig. 1 QQ plot of total length trait of C. argus 性状 SNP 位点 P 值从小到大排序,得到 6 个 P 值