Page 46 - 《水产学报》2025年第11期
P. 46
王海山,等 水产学报, 2025, 49(11): 119104
表 3 蛋白质编码基因构建 BI 及 ML 树最佳分区模型
Tab. 3 The optimal partition models of BI and ML
贝叶斯(BI)法 MrBayes 最大似然(ML)法 IQ TREE
分区 分区
area 基因 最佳模型 area 基因 最佳模型
genes optimal models genes optimal models
1 ATP6, COX1 GTR+F+I+G4 1 ATP6, COX1 GTR+F+I+G4
2 ATP8, COX2, ND4L HKY+F+G4 2 ATP8, COX2, ND4L HKY+F+G4
3 COX3, ND2, ND3 HKY+F+I+G4 3 COX3, ND2, ND3 HKY+F+I+I+R3
4 CYTB GTR+F+I+G4 4 CYTB TIM2+F+I+G4
5 ND1, ND4, ND5 GTR+F+I+G4 5 ND1, ND4, ND5, ND6 GTR+F+I+I+R3
6 ND6 HKY+F+I+G4
උ`genus 变色蜒螺 N. chamaeleon
Divia 矮狮蜒螺 N. histrio
红唇蜒螺`N. signata
Theodoxus 滑圆蜒螺 N. ocellata
Vitta 环纹蜒螺`N. balteata
ґඋ`Clithon 虚线蜒螺 N. insculpta
උ`Nerita 黑肋蜒螺`N. costata
уඋ`Septaria 褶蜒螺`N. plicata
波纹蜒螺`N. undata
ފඋ`Neritina 四齿蜒螺`N. versicolor
游螺属 Neripteron 日本蜒螺 N. japonica
齿纹蜒螺 N. yoldii
自展值 bootstrap 光荣蜒螺 N. fulgurans
棋盘蜒螺 N. tessellata
50.0
62.5 玄武蜒螺 N. melanotragus
小皇冠彩螺 C. corona
75.0 C. lentiginosum
87.5
100.0 转色彩螺 C. retropictum
糙鳞彩螺 C. squarrosum
多色彩螺 C. sowerbianum
奥莱彩螺 C. oualaniense
V. usnea
S. lineata
N.violaceum
紫游螺 N. violacea
N. iris
T. fluviatilis
0.1
D. briandi
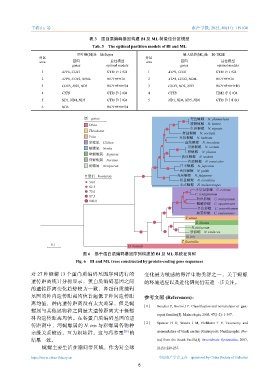
图 6 基于蛋白质编码基因序列构建的 BI 及 ML 系统发育树
Fig. 6 BI and ML trees constructed by protein-coding gene sequences
对 27 种蜒螺 13 个蛋白质编码基因序列进行的 变化最为敏感的海洋生物类群之一,关于蜒螺
遗传距离统计分析显示,蛋白质编码基因之间 的环境适应以及进化研究仍需进一步关注。
的遗传距离变化趋势较为一致,各蛋白质编码
基因的种内遗传距离均值普遍低于种间遗传距 参考文献 (References):
离均值,种内遗传距离没有太大差异,但是蜒
[ 1 ] Bouchet P, Rocroi J P. Classification and nomenclator of gast-
螺属与其他属物种之间最大遗传距离大于蜒螺
ropod families[J]. Malacologia, 2005, 47(1-2): 1-397.
科内遗传距离均值。在各蛋白质编码基因的遗
传距离中,河蜒螺属的 N. iris 与彩螺属各物种 [ 2 ] Spencer H G, Waters J M, Eichhorst T E. Taxonomy and
亲缘关系较近,互为姐妹群,这与冯鉴童 [25] 的 nomenclature of black nerites (Gastropoda: Neritimorpha: Ner-
结果一致。 ita) from the South Pacific[J]. Invertebrate Systematics, 2007,
蜒螺主要生活在潮间带区域,作为对全球 21(3): 229-237.
https://www.china-fishery.cn 中国水产学会主办 sponsored by China Society of Fisheries
8